# Filtering genomic variants
for variant in vcf.fetch('chr1', 1000, 2000):
if variant.QUAL > 30:
process_sample(variant.samples[0])
# Plotting allele frequencies
ggplot(aes(x=pos, y=freq)) +
geom_line(color="#0ea5e9") +
theme_minimal()
# Filtering genomic variants
for variant in vcf.fetch('chr1', 1000, 2000):
if variant.QUAL > 30:
process_sample(variant.samples[0])
# Plotting allele frequencies
ggplot(aes(x=pos, y=freq)) +
geom_line(color="#0ea5e9") +
theme_minimal()
# Filtering genomic variants
for variant in vcf.fetch('chr1', 1000, 2000):
if variant.QUAL > 30:
process_sample(variant.samples[0])
# Plotting allele frequencies
ggplot(aes(x=pos, y=freq)) +
geom_line(color="#0ea5e9") +
theme_minimal()
# Filtering genomic variants
for variant in vcf.fetch('chr1', 1000, 2000):
if variant.QUAL > 30:
process_sample(variant.samples[0])
# Plotting allele frequencies
ggplot(aes(x=pos, y=freq)) +
geom_line(color="#0ea5e9") +
theme_minimal()
# Filtering genomic variants
for variant in vcf.fetch('chr1', 1000, 2000):
if variant.QUAL > 30:
process_sample(variant.samples[0])
# Plotting allele frequencies
ggplot(aes(x=pos, y=freq)) +
geom_line(color="#0ea5e9") +
theme_minimal()
# Filtering genomic variants
for variant in vcf.fetch('chr1', 1000, 2000):
if variant.QUAL > 30:
process_sample(variant.samples[0])
# Plotting allele frequencies
ggplot(aes(x=pos, y=freq)) +
geom_line(color="#0ea5e9") +
theme_minimal()
@TATAbox:~/workspace$ _
Ferramentas, modelos e scripts para a amnésia do futuro... if works → intencional; else → feature em construção produzida às 3h am. (Otimize ou julgue silenciosamente).
Diversidade de Vertebrados
~86 mil espécies em sunburst interativo com 3 níveis taxonômicos, silhuetas PhyloPic e escala log/linear.
Tree-Thinking com CladeX
Guia prático para não confundir mais grupos parafiléticos e entender onde os caracteres surgem na árvore.
Astro101: Introdução à Astronomia e Observação
Um guia inicial para os fundamentos da astronomia, tipos de telescópios e as primeiras observações noturnas.
> ~/projetos --list
Repositórios que sobreviveram ao rm -rf. Alguns são úteis, outros... (veja você mesmo).
Bioinfo Hub 5
kviewer
Visualização de k-mers. Porque ler arquivos de sequenciamento bruto sem ajuda visual é pedir para ter dor de cabeça.
ggrelated
Estimativa de parentesco sem sofrimento. Quem é parente de quem? Descubra antes que a árvore genealógica vire um círculo.
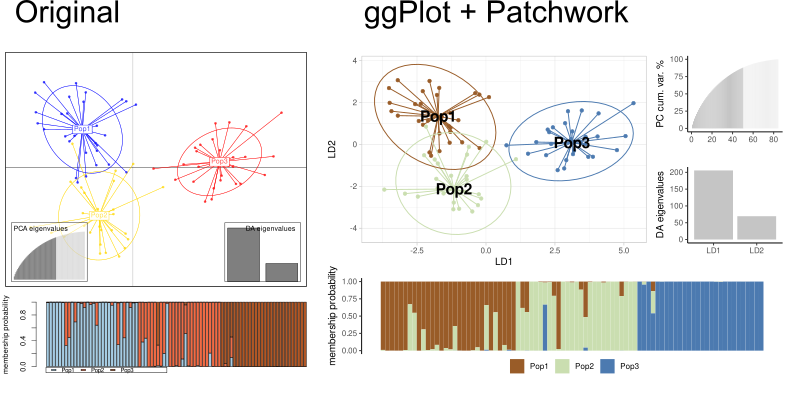
ggDAPC
DAPC visual. Agrupar populações nunca foi tão estético. Se os grupos não separarem, a culpa não é do gráfico.
Data Ecology 3
lsma
Análise de métricas de paisagem. Porque entender a forma do habitat é melhor do que apenas adivinhar.
ggmodel
Visualização de modelos estatísticos. Transforme outputs chatos do R base em superfícies ggplot2 que as pessoas realmente entendem.
R4eco
Scripts para ecologia quantitativa. O canivete suíço para quando você precisa processar dados ecológicos sem reinventar a roda.
Outros 3
> ~/papers
Tentando convencer os revisores de que meus dados fazem sentido. (Linkado via ORCID para minha própria sanidade mental).
DNA Barcoding Reveals a Critical Spawning Ground in the Paranapanema River Basin, Southern Brazil
Association of IL10 gene SNVs rs1800896 (A>G), rs1800871 (C>T), rs1800872 (C>A) and haplotypes with COVID-19 severity and outcome in the Brazilian population
Coastal-inland divergence and postglacial expansion in the populations of the orchid bee <i>Euglossa annectans</i>
Disentangled and Interpretable Multimodal Attention Fusion for Cancer Survival Prediction
Forest cover outweighs restoration strategy in explaining Euglossini beta diversity in the Atlantic Forest, Brazil
Gene polymorphisms associated with immunosuppression and their implications in the onset of cervical cancer
> ~/teaching --help
Materiais de aula e guias rápidos estruturados em trilhas de aprendizado.
Modelagem de Nicho Ecológico (ENM101)
Trilha prática para aprender a modelar distribuição de espécies no R, do zero à projeção.
Introdução ao R para Biólogos (R101)
Uma jornada para transformar café em gráficos elegantes (e erros de sintaxe) começando do zero.
Sistemática Filogenética e Tree-Thinking
Uma jornada para entender a genealogia da vida, desde a interpretação de ramos até a simulação de processos evolutivos.
Diversidade de Vertebrados
Sunburst interativo com ~86 mil espécies em 3 níveis taxonômicos. Útil para discutir desigualdade de biodiversidade, escalas log vs linear e a lógica da classificação filogenética.
> whoami --identity
Sou Biólogo com doutorado em Genética e Biologia Molecular. Meu trabalho transita entre a biologia evolutiva e a ciência da computação, com foco em ecologia molecular e análise de dados genômicos.
Atualmente, como Professor Associado na UENP, dedico meu tempo à pesquisa e ao desenvolvimento de ferramentas de código aberto para a comunidade científica.
Contato Direto
wilsonfrantine@gmail.com> ssh --connections
Reporte bugs, sugira melhorias (seja gentil) ou envie um ping. Latência inversamente proporcional ao nível de cafeína.